Scientific journal
Modern problems of science and education
ISSN 2070-7428
"Перечень" ВАК
ИФ РИНЦ = 0,936
MOLECULAR ANALYSIS OF PMP-GENES OF CHLAMYDIAL STRAIN PP-87, ENCODING POLYMORPHIC OUTER MEMBRANE PROTEINS
Pmp-гены, кодирующие полиморфные белки наружной мембраны хламидий (Polymorphic Outer Membrane Proteins – POMPs), включая функционально схожие белки-аналоги группы автотранспортеров, составляют до 14% всего генетического материала микроорганизма [1, 5].
Полиморфные белки наружной мембраны хламидий, в свою очередь, проявляющие высокую имунногенную активность, применяются при создании субъединичной (пептидной) противохламидийной вакцины [3, 8].
Полиморфизм pmp-генов ассоциирован с патогенетическими свойствами хламидий, их вирулентностью и тканевым тропизмом возбудителя [1, 4]. А методы полногеномного секвенирования способствуют раскрытию молекулярных механизмов его патогенеза [5, 7].
Цель настоящей работы – сравнительный молекулярно-генетический анализ pmp-генов штамма хламидий ПП-87, на основе полученных массивов данных полногеномного секвенирования.
Материалы и методы исследования
Экстракция геномной ДНК штамма хламидий ПП-87, выделенного от абортировавшей самки песца [2, 6], и адаптированного к размножению в желточных оболочках куриных эмбрионов, осуществлена набором «ДНК-сорб Б» («ЦНИИ эпидемиологии», Россия).
Создание фрагментной библиотеки выполнено с помощью набора NEBNext DNA Library (NEB, США), где на начальном этапе проводилась фрагментация геномной ДНК с помощью ультразвука на приборе Covaris S2 (Covaris, США). Далее полученные фрагменты обрабатывались Т4 ДНК-полимеразой для получения «тупых» концов и Т4 полинуклеотидкиназой для присоединения фосфата на 5'-конец. На следующем этапе в реакционную смесь был добавлен фрагмент Кленова для присоединения dА на 3'-конец, что позволило провести дальнейшее селективное присоединение к полученным фрагментам с помощью ДНК-лигазы двуцепочечного адаптера, несущего в своей последовательности участки для проведения полимеразной цепной реакции (ПЦР) и секвенирования. На последнем этапе проводилась ПЦР для увеличения копийности фрагментов, а также для избавления от концевых некомплементарных участков.
Качество полученной фрагментной библиотеки оценивали с помощью набора High Sensitivity DNA Kit на приборе Bioanalyzer 2100 (Agilent, США). Количество ДНК было определено с помощью набора dsDNA High Sensitivity Kit на флюориметре Qubit 1.0 (Invitrogene, США). Секвенирование фрагментной библиотеки на геномном секвенаторе MiSeq (Illumina, США) проводилось по протоколу производителя с использованием набора MiSeq Reagent Kit, 600 Cycles (Illumina, США) в ЦКП «Геномика» СО РАН (Новосибирск).
Результаты исследований и их обсуждение
В результате секвенирования были получены парные чтения длиной 300+300 нт с общим объемом данных порядка 660 тыс. последовательностей, 80% которых имели качество QV>30, эквивалентное 1 ошибке на 1000 нуклеотидов.
Для последующего анализа последовательности были отфильтрованы по качеству (QV>20), оттриммированы и картированы на референсный геном Chlamydia psittaci GR9 (GenBank A/N: CP003791). При этом, количество ридов, соответствовавших этому геному составило всего 1,6% с его покрытием в среднем 2±1,86. Значительная же доля просеквенированного материала – ДНК Gallus Gallus, послужившая причиной низкого покрытия генома хламидий.
Данное обстоятельство не помешало провести анализ идентичности штамма Chlamydia sp. ПП-87 к штаммам Chlamydia psittaci GR9 (CP003791), Chlamydia psittaci 6BC (CP002549) и Chlamydia abortus S26/3 (CR848038) в процентном выражении выборок локусов pmp-генов, представленный в развернутой табличной форме (табл. 1).
Таблица 1
Анализ идентичности штамма Chlamydia sp. ПП-87 к штаммам C. psittaci GR9, C. psittaci 6BC и C. abortus S26/3 в процентном выражении выборок локусов pmp-генов
|
Chlamydia sp. ПП-87 vs Chlamydia psittaci 6BC |
GR 6BC |
Chlamydia sp. ПП-87 vs Chlamydia psittaci GR9 |
GR9 S26/3 |
Chlamydia sp. ПП-87 vs Chlamydia abortus S26/3 |
|
complement(217354..222747) /gene="pmp1B" /locus_tag="CPSIT_0231" /product="polymorphic outer membrane protein B family" (219145-219769) 92% (222386-222832) 100% |
97 % |
complement(217331..222727)
/locus_tag="B598_0234" /product="autotransporter beta-domain protein (219034-219659) 100% (222275-222721) 100% |
92 % |
complement(217265..222631) /gene="pmp1B" /locus_tag="CAB200" /product="polymorphic outer membrane protein" (218971-219591) 95% (222188-222625) 87% |
|
complement(223038..225839) /gene="pmp2A" /locus_tag="CPSIT_0232" /product="polymorphic outer membrane protein A family" (223082-223375) 99% (225356-225839) 100% |
99 % |
complement(222927..225728)
/locus_tag="B598_0235" /product="autotransporter beta-domain protein" (222971-223264) 100% (225245-225728) 100% |
92 % |
complement(222833..225634) /gene="pmp2A" /locus_tag="CAB201" /product="polymorphic outer membrane protein" (222877-223170) 95% (225153-225634) 93% |
|
complement(293986..296988) /gene="pmp3E" /locus_tag="CPSIT_0297" /product="polymorphic outer membrane protein E family" (293986-294231) 95% (296305-296867) 91% |
90 % |
complement(293489..296485)
/locus_tag="B598_0301" /product=”autotransporter beta domain protein” (293489-293734) 99% (295801-296366) 100% |
86 % |
complement(293548..296514) /gene="pmp3E" /locus_tag="CAB265" /product="polymorphic outer membrane lipoprotein" (293548-293793) 86% (295829-296395) 72% |
|
complement(297010..299895) /gene="pmp4E" /locus_tag="CPSIT_0298" /product="polymorphic outer membrane protein E family" (297010-297564) 89% (299258-299895) 100% |
96 % |
complement(296507..299392)
/locus_tag="B598_0302" /product="autotransporter beta-domain protein" (296507-297061) 100% (298755-299392) 100% |
82 % |
complement(296536..299397) /gene="pmp4E" /locus_tag="CAB266" /product="polymorphic outer membrane protein" (296536-297090) 88% (298751-299397) 83% |
|
complement(300162..301226) /gene="pmp5E" /locus_tag="CPSIT_0300" /product="polymorphic outer membrane autotransporter beta-domain protein" (300162-301226) 99% |
99 % |
complement(299660..300724)
/locus_tag="B598_0303" /product="autotransporter beta-domain protein"
(299660-300724) 99% |
81 % |
complement(299664..300743) /gene="pmp5E" /locus_tag="CAB267" /product="polymorphic outer membrane protein"
(299664-300743) 81% |
|
complement(301687..304641) /gene="pmp6H" /locus_tag="CPSIT_0301" /product="polymorphic outer membrane protein H family" (301687-303038) 97% (304190-304641) 98% |
96 % |
complement(301185..304139)
/locus_tag="B598_0305" /product="autotransporter beta-domain protein (301185-302539) 100% (303688-304139) 99% |
88 % |
complement(301197..304139) /gene="pmp6H" /locus_tag="CAB268" /product="polymorphic outer membrane protein" (301197-302548) 88% (303691-304139) 93% |
|
complement(304667..307798) /gene="pmp7G" /locus_tag="CPSIT_0302" /product="polymorphic outer membrane protein G family"
(304667-305146) 99% (306510-307228) 93% |
96 % |
complement(304165..307284)
/locus_tag="B598_0306" /product="outer membrane autotransporter barrel domain protein" (304165-304644) 100% (306005-306714) 100% |
88 % |
complement(304165..307239) /gene="pmp7G" /locus_tag="CAB269" /product="polymorphic outer membrane protein"
(304165-304644) 94% (305993-306669) 87% |
|
complement(308031..310586) /gene="pmp8G" /locus_tag="CPSIT_0304" /product="polymorphic outer membrane protein G family"
(308059-308652) 99% (310248-310586) 99% |
99 % |
complement(307518..310073)
/locus_tag="B598_0307" /product="autotransporter beta-domain protein"
(307546-308139) 99% (309735-310073) 100% |
88 % |
complement(307520..310121) /gene="pmp8G" /locus_tag="CAB270" /product="polymorphic outer membrane protein (pseudogene)" (307548-308141) 90% (309735-310070) 91% |
|
complement(310842..313676) /gene="pmp9G" /locus_tag="CPSIT_0305" /product="polymorphic outer membrane protein G family"
(310922-311474) 99% (312659-313254) 94% |
96 % |
complement(310328..313162)
/locus_tag="B598_0308" /product="autotransporter beta-domain protein"
(310408-310960) 100% (312145-312740) 100% |
86 % |
complement(310327..313154) /gene="pmp9G" /locus_tag="CAB273" /product="polymorphic outer membrane protein (pseudogene)" (310407-310959) 89% (312137-312732) 86% |
|
complement(313808..316330) /gene="pmp10G" /locus_tag="CPSIT_0306" /product="polymorphic outer membrane protein G family" (313808-314672) 99% (314724-315874) 99% |
99 % |
complement(313293..315815)
/locus_tag="B598_0309" /product="autotransporter beta-domain protein" (313293-314157) 100% (314209-315359) 100% |
92 % |
complement(313284..315806) /gene="pmp10G" /locus_tag="CAB277" /product="polymorphic outer membrane protein" (313284-314148) 93% (314200-315350) 92% |
|
complement(316486..319020) /gene="pmp11G" /locus_tag="CPSIT_0307" /product="polymerase outer membrane protein G family"
(316684-317838) 99% (318465-319035) 99% |
99 % |
complement(315971..318520)
/locus_tag="B598_0310" /product="outer membrane autotransporter barrel domain protein" (316169-317323) 100% (317950-318520) 99% |
91 % |
complement(315962..318511) /gene="pmp11G" /locus_tag="CAB278" /product="polymorphic outer membrane protein"
(316160-317314) 91% (317941-318511) 93% |
|
complement(319411..321975) /gene="pmp12G" /locus_tag="CPSIT_0309" /product="polymorphic outer membrane protein G family"
(320158-320380) 95% (320910-321881) 77% |
81 % |
complement(319496..321508)
/locus_tag="B598_0313" /product=" chlamydia polymorphic membrane middle domain protein" (319706-319928) 96% (320444-321414) 100%\
(319706-319928) 96% (320444-321414) 100% |
79 % |
complement(318850..321371) /gene="pmp12G" /locus_tag="CAB279" /product="polymorphic outer membrane protein (pseudogene)" (319597-319819) 88% (320340-321277) 71%
(319597-319819) 88% (320340-321277) 71% |
|
complement(324766..327309) /gene="pmp14G" /locus_tag="CPSIT_0311" /product="polymorphic outer membrane protein G family" (325513-325735) 98% (326251-327215) 93% |
93 % |
|||
|
complement(322106..324637) /gene="pmp13G" /locus_tag="CPSIT_0310" /product="polymorphic outer membrane protein G family"
(322122-322933) 84% (323411-324637) 77% |
79 % |
complement(321639..322565) /locus_tag="B598_0314" /product="autotransporter beta-domain protein" complement(322936..324195) /locus_tag="B598_0315" /product=" chlamydia polymorphic membrane family protein" (321655-322466) 98% (322951-324195) 97%
(321655-322466) 98% (322951-324195) 97% |
82 % |
complement(321502..324045) /gene="pmp13G" /locus_tag="CAB281" /product="polymorphic outer membrane protein
(321518-322326) 83% (322815-324045) 80%
(321518-322326) 83% (322815-324045) 80% |
|
complement(327440..330007) /gene="pmp15G" /locus_tag="CPSIT_0312" /product="polymorphic outer membrane protein G family" (327456-328267) 97% (328754-330007) 91% |
95 % |
|||
|
complement(324766..327309) /gene="pmp14G" /locus_tag="CPSIT_0311" /product="polymorphic outer membrane protein G family"
(325669-326162) 24% (326221-326878) 50% |
46 % |
complement(324319..327099)
/locus_tag="B598_0317" /product="outer membrane autotransporter barrel domain protein" (325207-325700) 100% (325762-326422) 99%
(325207-325700) 100% (325762-326422) 99% |
93 % |
complement(324168..326948) /gene="pmp14G" /locus_tag="CAB282" /product="polymorphic outer membrane protein"
(325056-325549) 93% (325611-326271) 91%
(325056-325549) 93% (325611-326271) 91% |
|
complement(330131..332827) /gene="pmp16G" /locus_tag="CPSIT_0313" /product="polymorphic outer membrane protein G family" (331019-331512) 99% (331574-332234) 99% |
99 % |
|||
|
complement(327440..330007) /gene="pmp15G" /locus_tag="CPSIT_0312" /product="polymorphic outer membrane protein G family"
(327748-329521) 6% |
23 % |
complement(327243..331313)
/locus_tag="B598_0318" /product="outer membrane autotransporter barrel domain protein" (329154-330840) 100%
(329154-330840) 100% |
88 % |
complement(327092..331228) /gene="pmp15G" /locus_tag="CAB283" /product="polymorphic outer membrane protein"
(329012-330665) 84%
(329012-330665) 84% |
|
complement(333055..335394) /gene="pmp17G" /locus_tag="CPSIT_0314" /product="polymorphic outer membrane protein G family" (334963-336639) 89% complement(335706..337112) /gene="pmp18G" /locus_tag="CPSIT_0316" /product="polymorphic outer membrane protein G family" |
93 % |
|||
|
complement(330131..332827) /gene="pmp16G" /locus_tag="CPSIT_0313" /product="polymorphic outer membrane protein G family"
(331233-332229) 1% |
0 % |
691252..693760
/locus_tag="B598_0667" /product="chlamydia polymorphic membrane family protein" (691297-692233) 96%
(691297-692233) 96% |
81 % |
683361..685902 /gene="pmp16G" /locus_tag="CAB596" /product="polymorphic outer membrane protein (pseudogene)" (683406-684366) 81%
(683406-684366) 81% |
|
707548..710061 /gene="pmp19G" /locus_tag="CPSIT_0666" /product="polymorphic outer membrane protein G family" (707593-708529) 96% |
99 % |
|||
|
complement(333055..335394) /gene="pmp17G" /locus_tag="CPSIT_0314" /product="polymorphic outer membrane protein G family"
(334613-335042) 0% |
1 % |
693891..695195
/locus_tag="B598_0669" /product="chlamydia polymorphic membrane family protein" (694155-694553) 90%
(694155-694553) 90% |
79 % |
686033..688552 /gene="pmp17G" /locus_tag="CAB598" /product="polymorphic outer membrane protein"
(686282-686680) 84%
(686282-686680) 84%
(687836-688439) 90% |
|
710192..712741 /gene="pmp20G" /locus_tag="CPSIT_0667" /product="polymorphic outer membrane protein G family" (710456-710854) 90% |
100 % |
|||
|
712872..715415 /gene="pmp21G" /locus_tag="CPSIT_0668" /product="polymorphic outer membrane protein G family" (714699-715302) 99% |
100 % |
695847..696563
/locus_tag="B598_0671" /product="autotransporter beta-domain protein" (695847-696450) 99% |
91 % |
|
|
complement(926701..931305) /gene="pmp22D" /locus_tag="CPSIT_0856" /product="polymorphic outer membrane protein D family"
(926975-927345) 91% (930464-931055) 89% |
90 % |
complement(902244..906845)
/locus_tag="B598_0860" /product="outer membrane autotransporter barrel domain protein" (902518-902888) 100% (906001-906592) 100% |
98 % |
complement(899562..904163) /gene="pmp18D" /locus_tag="CAB776" /product="polymorphic outer membrane protein"
(899836-900206) 96% (903319-903910) 97% |
Данные, представленные в таблице 1, послужили основой для построения обобщенной таблицы анализа гетерогенности штамма ПП-87 к штаммам GR9, 6BC и S26/3 (табл. 2).
Таблица 2
Анализ гетерогенности штамма Chlamydia sp. ПП-87 к штаммам C. psittaci GR9, 6BC и C. abortus S26/3 в процентном выражении выборок локусов pmp-генов
|
Штамм |
Гетерогенность выборок локусов генов pmp1B-pmp9G |
||||||||
|
S26/3 |
5-13% pmp1B |
5-8% pmp2A |
14-28% pmp3E |
12-17% pmp4E |
19% pmp5E |
3-12% pmp6H |
6-13% pmp7G |
9-10% pmp8G |
11-14% pmp9G |
|
GR9 |
0% |
0% |
0-1% |
0% |
1% |
0-1% |
0% |
0-1% |
0% |
|
6BC |
0-8% pmp1B |
0-1% pmp2A |
5-9% pmp3E |
0-11% pmp4E |
1% pmp5E |
2-3% pmp6H |
1-7% pmp7G |
1% pmp8G |
1-6% pmp9G |
|
Штамм |
Гетерогенность выборок локусов генов pmp10G-pmp22D |
||||||||
|
S26/3 |
7-8% pmp10G |
7-9% pmp11G |
12-29% pmp12G |
17-20% pmp13G |
7-9% pmp14G |
16% pmp15G |
19% pmp16G |
10-16% pmp17G |
3-4 pmp18D |
|
GR9 |
0% |
0-1% |
0-4% |
2-3% |
0-1% |
0% |
4% |
1-10% |
0% |
|
6BC |
1% pmp10G |
1% pmp11G |
8-23% pmp12G (2-7%) (pmp14G) |
16-23% pmp13G (2-3%) (pmp15G) |
50-76% pmp14G (1%) (pmp16G) |
94% pmp15G (11%) (pmp17G) (pmp18G) |
99% pmp16G (4%) (pmp19G)
|
100% pmp17G [1-10%) (pmp20G) [pmp21G] |
(9-11%) (pmp22D)
|
Вышеприведенный анализ гетерогенности/идентичности по выборкам локусов pmp-генов (табл. 2/1) наглядно продемонстрировал близкородственное сходство штамма ПП-87 к референсному штамму Chlamydia psittaci GR9, но с существенными нуклеотидными различиями, достигающими 10% гетерогенности по отношению к соответствующему локусу B598_0669 штамма GR9 (выборка: 694155-694553 nt).
Полученный результат выравнивания соответствующих нуклеотидных последовательностей, отраженный на рисунке 1, проведенный с целью прояснения причины вышеотмеченной существенной гетерогенности, указывает на возможное эволюционное формирование анализируемого локуса pmp-гена штамма ПП-87 под влиянием межштаммовой/межгенной pmp рекомбинации.
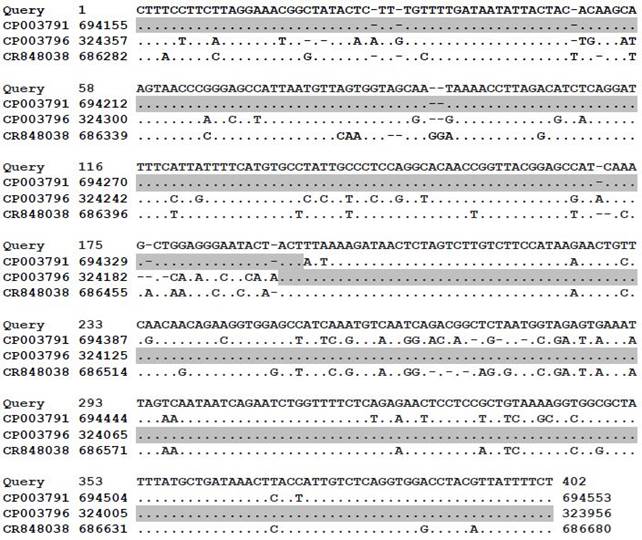
Рис. 1. Выравнивание нуклеотидных последовательностей локуса pmp17G/pmp20G-гена штаммов Chlamydia sp. ПП-87 (Query), Chlamydia psittaci GR9 (CP003791), Chlamydia abortus S26/3 (CR848038) и локуса pmp13G-гена Chlamydia psittaci WC (CP003796).
Примечания: Серым цветом выделены последовательности штаммов GR9 и WC, гомологичные соответствующим последовательностям штамма ПП-87.
Дополнительный анализ гетерогенности референсного штамма GR9 к штаммам 6BC и S26/3 в процентном выражении pmp-генов показал меньшую гетерогенность (или большую идентичность) GR9 к 6BC по подавляющему большинству анализируемых генов, за исключением pmp18D-гена штамма S26/3, к которому штамм GR9 по соответствующему локусу B598_0860 проявляет наиболее близкородственное сходство, нежели чем к аналогичному pmp22D-гену 6BC (табл. 3).
Таблица 3
Анализ гетерогенности штамма C. psittaci GR9 к штаммам С. psittaci 6BC и C. abortus S26/3 в процентном выражении pmp-генов
|
Штамм |
Гетерогенность выборок локусов генов pmp1B-pmp9G |
||||||||
|
S26/3 |
8% pmp1B |
8% pmp2A |
14% pmp3E |
18% pmp4E |
9% pmp5E |
12% pmp6H |
12% pmp7G |
12% pmp8G |
14% pmp9G |
|
6BC |
3% pmp1B |
1% pmp2A |
10% pmp3E |
4% pmp4E |
1% pmp5E |
4% pmp6H |
4% pmp7G |
1% pmp8G |
4% pmp9G |
|
Штамм |
Гетерогенность выборок локусов генов pmp10G-pmp22D |
||||||||
|
S26/3 |
8% pmp10G |
9% pmp11G |
21% pmp12G |
18% pmp13G |
7% pmp14G |
12% pmp15G |
19% pmp16G |
9-21% pmp17G |
2% pmp18D |
|
6BC |
1% pmp10G |
1% pmp11G |
19% pmp12G |
21% pmp13G |
54% pmp14G |
77% pmp15G |
100% pmp16G |
99% pmp17G |
(10%) (pmp22D)
|
|
(7%) (pmp14G) |
(5%) (pmp15G) |
(1%) (pmp16G) |
(7%) (pmp17G) (pmp18G) |
(1%) (pmp19G) |
(0%) (pmp20G) [pmp21G] |
||||
Следует отметить, что по анализируемым выборкам (902518-902888 nt, 906001-906592 nt) локуса B598_0860 штамм GR9 имеет 100% идентичность с ПП-87, который, в свою очередь, аналогично референсному штамму, тоже проявляет близкородственное сходство к S26/3 (pmp18D-ген, локус CAB776, выборки: 899836-900206 nt, 903319-903910 nt), нежели чем к 6BC (pmp22D-ген, локус CPSIT_0856, выборки 926975-9273 nt, 45930464-931055 nt) (табл. 1).
Заключение
Таким образом, установлено, что проанализированные в данной работе pmp-гены, кодирующие полиморфные белки наружной мембраны штамма Chlamydia sp. ПП-87, имеют наряду с референсным штаммом Chlamydia psittaci GR9 по подавляющему большинству представленных генов близкородственное сходство к типовому штамму Chlamydia psittaci 6BC, нежели чем к штамму Chlamydia abortus S26/3, за исключением pmp18D-гена последнего, являющегося одним из ключей к раскрытию молекулярных механизмов развития инфекционного процесса с обоснованием патогенеза хламидийной инфекции, ассоциированной с колонизацией плаценты хозяина внутриклеточным паразитом, и прояснению эволюции хламидий.
Рецензенты:
Госманов Р.Г., д.вет.н., профессор кафедры микробиологии, вирусологии и иммунологии Казанской государственной академии ветеринарной медицины имени Н.Э. Баумана, г. Казань.
Якупов Т.Р., д.вет.н., доцент кафедры биологической и неорганической химии Казанской государственной академии ветеринарной медицины имени Н. Э. Баумана, г. Казань.
Библиографическая ссылка
Каримов М.З., Бакиров И.Х., Вафин Р.Р., Равилов Р.Х., Тюлькин С.В., Тупикин А.Е., Ахметов Т.М. МОЛЕКУЛЯРНЫЙ АНАЛИЗ PMP-ГЕНОВ ШТАММА ХЛАМИДИЙ ПП-87, КОДИРУЮЩИХ ПОЛИМОРФНЫЕ БЕЛКИ НАРУЖНОЙ МЕМБРАНЫ // Современные проблемы науки и образования. 2015. № 6. ;URL: https://science-education.ru/en/article/view?id=23246 (дата обращения: 16.05.2026).



